目录
- 1. eggNOG简介
- 2. eggNOG-Mapper注释原理
- 3. eggNOG 5.0数据资源
- 4. eggNOG-Mapper使用
- 5. NOG、KOG、COG、KEGG、GO区别?
1. eggNOG简介
最近考虑到所用的一些数据库太旧了,需要更新。在整理的时候发现eggNOG数据库在去年的时候已经做了一次更新eggNOG 5.0: a hierarchical, functionally and phylogenetically annotated orthology resource based on 5090 organisms and 2502 viruses。距离上个版本eggNOG4.5已经过去了3-4年,更新频率相对来说比较慢。但这次更新的内容是翻倍式增加的,以下是4.5和5.0比较。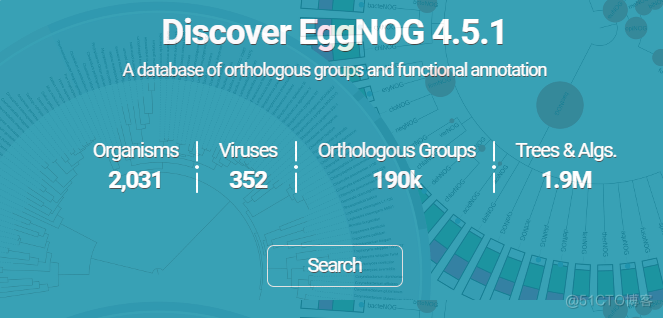

eggNOG数据库全称是:直系同源蛋白分组比对(evolutionary genealogy of genes: Non-supervised Orthologous Groups)数据库,由EMBL创建维护,是对NCBI的COG数据库进行拓展,提供不同分类水平蛋白的直系同源分组(Orthologous Groups,OG),包括真核、原核及病毒的数据信息。它扩展了COG数据库的分类方法,采用无监督聚类算法在全基因组范围内推导基因功能,更适用于谱系特征基因的分析。
2. eggNOG-Mapper注释原理
常规功能注释方法基于序列相似性寻找直系同源基因,常用blast+blast2go或InterProscan来注释,这种方法可能找到旁系同源基因,而eggNOG能区分旁系和直系同源基因,因此开发出eggNOG-mapper来进行功能注释。eggNOG v5.0对应的工具是eggNOG-mapper v2。
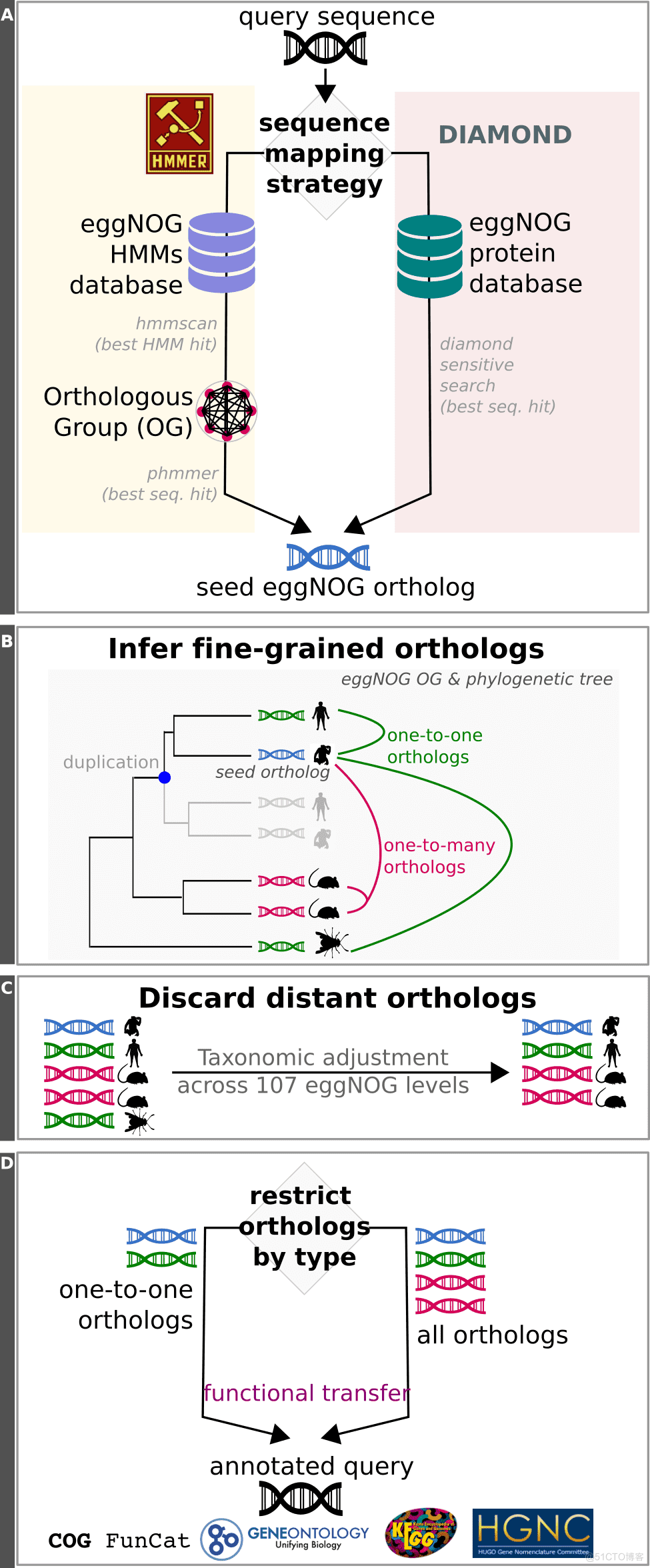
注释的过程可分为图下四个过程:
- A. 序列比对:通过HMMER搜索HMMs数据库找到OG,或者通过DIAMOND搜索蛋白数据库(速度更快,更适合宏组学),每条序列的最佳匹配结果以 seed ortholog 形式存放,用于获取其他直系同源基因。
- B. 获取直系同源基因:通过seed ortholog来提取一个或一组精细的直系同源基因。
- C.去除关系较远的直系同源基因:根据bit-score或E-value对结果进行一次过滤,剔除同源性不高的结果。
- D. 功能注释:蛋白序列搜索到的直系同源基因的功能描述就是最终的注释结果,如GO、KEGG、COG等。
3. eggNOG 5.0数据资源
数据库是生物信息的基础,每个生物数据库都有各自的特点(主要是从不同角度说明生物问题),但信息的全面、分类和准确性是数据库的关键。eggNOG 5.0的下载数据在:http://eggnog5.embl.de/download/eggnog_5.0/
其中e5.proteomes.faa为所有的蛋白组序列,e5.viruses.faa为所有的病毒蛋白序列,e5.taxid_info.tsv为Taxid对应的物种名称以及完整的谱系信息,e5.og_annotations.tsv为所有的NOG信息,其第一列为Taxid,第二列为NOG groups,第三列为COG归属,第四列为Function。
除了功能,每个物种都有相应的注释信息http://eggnog5.embl.de/download/eggnog_5.0/per_tax_level/,比如1060(TaxID):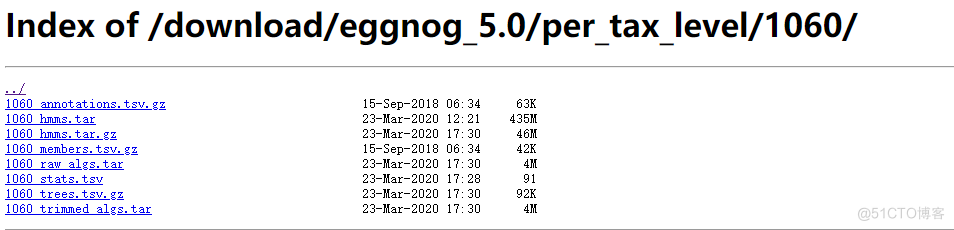
5000余个物种对功能注释来说是比较全面的了,但如果要做物种注释,那是远远不够的。
4. eggNOG-Mapper使用
在eggnog-mapper使用之前应该准备好:python、hmmer、diamond、fasta、注释数据库。
# 下载软件
git clone https://github.com/jhcepas/eggnog-mapper.git
# 下载数据库
cd eggnog-mapper ./download_eggnog_data.py euk #euk真核,bact原核,arch古菌,viruses病毒
#注释
python emapper.py -i test.fa --output ./ -d euk #默认以HMMER搜索
python emapper.py -m diamond -i test.fa --output ./ -d euk #指定搜索数据库类型,可大类、小类
python emapper.py -i test.fa --output ./ -d maNOG #哺乳动物NOG
python emapper.py -i test.fa --output ./ -d maNOG --usemem --cpu 10 #内存和线程
至于eggNOG注释的结果,包括了一些匹配和得分信息,以及GO,KEGG,BiGG,COG,KOG,NOG等功能注释结果。但不建议用它的GO和KEGG结果,因为这两个数据库是生信领域更新最快的,信息最全,eggNOG注释的结果可能会跟不上。可以采纳下它的COG、KOG、NOG的注释信息,因为COG/KOG几乎没有更新了,还停留在2003-2014年:https://www.ncbi.nlm.nih.gov/COG/。
5. NOG、KOG、COG、KEGG、GO区别?
KEGG(Encyclopedia of Genes and Genomes)和GO(Gene Ontology)耳熟能详就不解释了,至少是目前权威公认的两大数据库。
主要是NOG和KOG、COG有点懵。
相同点:三者都是同源分类数据库,即都是OG(Orthologous Groups)。
不同点:
- COG:Clusters ofOrthologousGroups of proteins,即同源蛋白簇,是NCBI的一个数据库。根据生物完整基因组的编码蛋白系统进化关系分类构建而成,每一簇COG由直系同源序列构成,从而可以推测该序列的功能,按功能共可以分为二十六类。
- KOG:EuKaryoticOrthologousGroups(为什么不叫EOG?问号脸)。广义上COG分为真核和原核生物两类,原核的一般称为COG数据库,真核的一般称为KOG数据库。
- NOG:Non-supervisedOrthologousGroups,注意是非监督,因COG未及时更新,EMBL EggNOG对COG进行了完善,极大拓展了基因组信息,主要是基于HMM分析提供更细致的OG分析。
做了eggNOG,还有必要做COG/KOG吗?做不做都可以,主要看心情,看哪个更能解释你的生物学问题。一般来说,差别不会太大,COG虽然过时,但权威性还在呀。
附:不同功能数据库的层级划分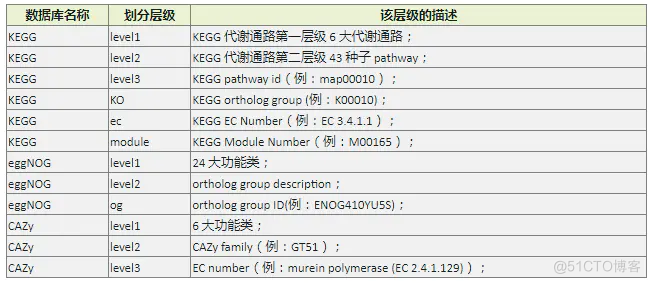
Ref:
应该是最好的eggnog-mapper功能注释教程时隔四年,NOG数据库更新啦!宏基因组功能注释(以COG为例)https://www.biostars.org/p/286615/
作者:Bioinfarmer。若要及时了解动态信息,请关注同名微信公众号:Bioinfarmer。
【文章转自:扬州机房 http://www.558idc.com/yz.html欢迎留下您的宝贵建议】
